# install.packages(c('tidyverse','sf','terra','tmap','remotes','geodata','rstac','earthdatalogin))
# remotes::install_github("ODES-Chile/agrometR")Taller 1: Ejemplo
Preparación de los datos
1 Setup
1.1 Instalar paquetes de R
1.2 Cargar paquetes de R
library(remotes) #paquete que trae función para instala un paquete desde github
library(tidyverse) #colección de paquetes para análisis de datos
library(sf) #manejo de datos vectoriales
library(terra) #manejo de datos raster y vectoriales
library(tmap) # creación de mapas temáticos
library(geodata) # acceso a descarga de diferentes datos raster y vectoriales
library(rstac) # acceder a spatial temporal assets catalogs (STAC)
library(agrometR) #acceder a datos de estaciones red Agromet
library(earthdatalogin) #para acceder a productos NASA 'EarthData' 2 Prepara datos vectoriales área de estudio
Descargar datos vectoriales de límites administrativos
#descarga límites administrativos a nivel de regiones para Chile
regiones <- geodata::gadm('chile',path = 'data/raw')
#convierte entre clase spatVector a sf
regiones_sf <- regiones |>
sf::st_as_sf()
#clase del objeto regiones_sf
class(regiones_sf)[1] "sf" "data.frame"# hacer un mapa de las geometrias de las regiones
plot(sf::st_geometry(regiones_sf))
regiones_sf$NAME_1 [1] "Antofagasta" "Araucanía"
[3] "Arica y Parinacota" "Atacama"
[5] "Aysén del General Ibañez del Cam" "Bío-Bío"
[7] "Coquimbo" "Libertador General Bernardo O'Hi"
[9] "Los Lagos" "Los Ríos"
[11] "Magallanes y Antártica Chilena" "Maule"
[13] "Ñuble" "Santiago Metropolitan"
[15] "Tarapacá" "Valparaíso" #selecciona las regiones entre Copquimbo y Araucania
regs <- regiones_sf[c(2,6,7,8,12,13,14,16),] #selecciona la geometria (fila) 16 que corresponde a la región de Valparaiso
plot(sf::st_geometry(regs))
#extensión para cortar para chile continental
e <- c(xmin= -73.95,ymin=-40,xmax=-69.5,ymax=-28.9)
ext_sf <- e |>
sf::st_bbox() |>
sf::st_as_sfc() |>
sf::st_as_sf(crs = 4326) regs_con <- sf::st_intersection(regs,ext_sf)Warning: attribute variables are assumed to be spatially constant throughout
all geometries#une todas las regiones para quedar con un poligono con los límites entre Coquimbo y Araucania y se queda con la geometria
regs_con <- sf::st_union(regs_con) |>
sf::st_geometry()
#mapa de la geometria
plot(sf::st_geometry(regs_con))
3 Preparar predictores rasters
3.1 Preparar predictores de elevación
#centroide de la región de Valparaiso
coords <- regs_con |>
sf::st_centroid()|> # función de centroide devuelve un objeto sf
sf::st_coordinates() # convierte el objeto sf en matrix
#descargar elevación a resolución de 30 segundos
elev <- geodata::elevation_30s('chile',path='data/raw')
#cortar y aplicar mascara para la región de interés
elev_regs <- terra::crop(elev,regs_con)
elev_regs <- terra::mask(elev_regs,sf::st_as_sf(regs_con))
#mapa de elevación
plot(elev_regs)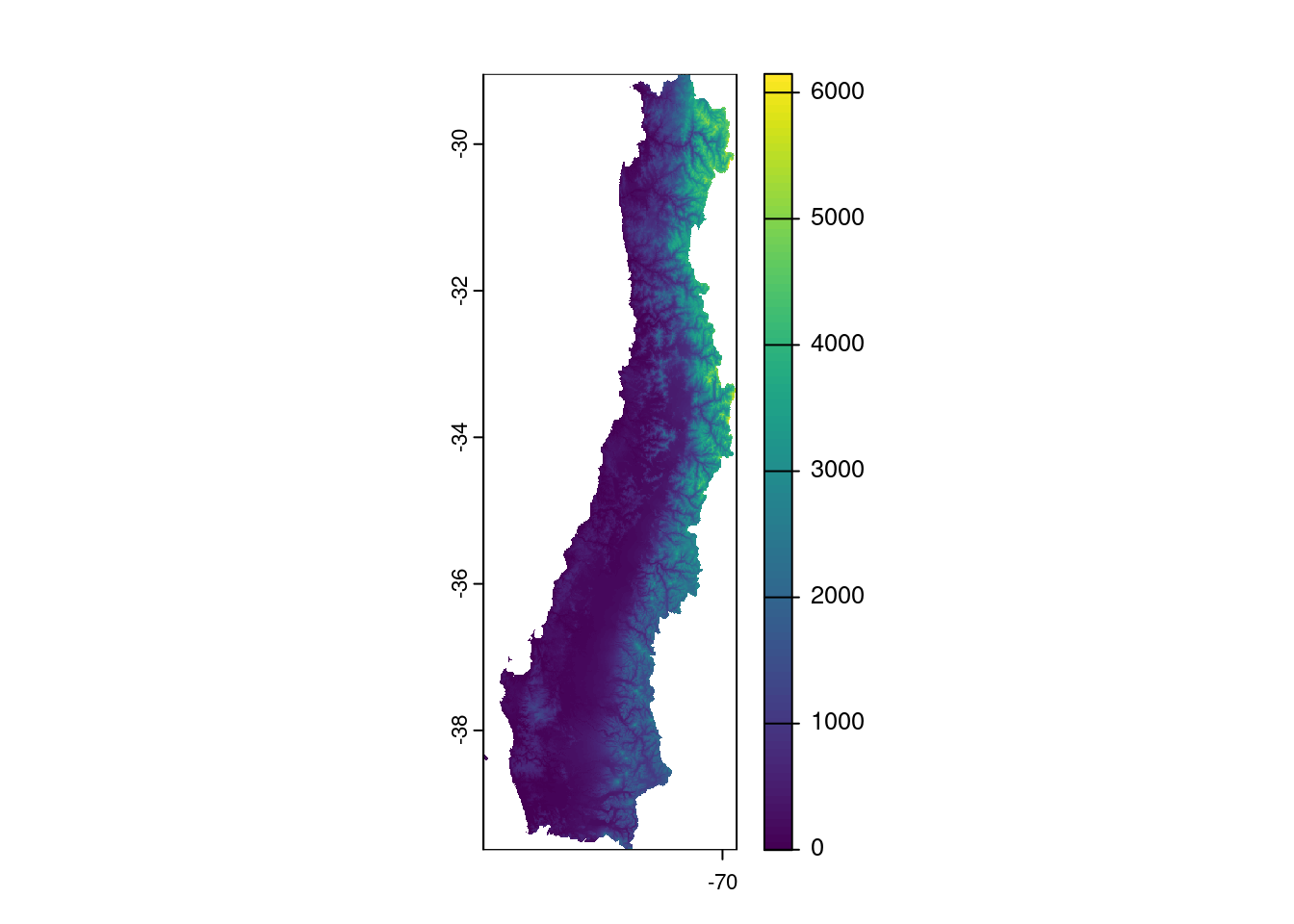
# reproyectar objeto raster a 32719 UTM zona 19S datum WGS84
elev_proj <- terra::project(elev_regs,"EPSG:32719")
#reproyecta objeto vectorial sf a utm zona 19S datum WGS84
regs_utm <- regs_con |>
sf::st_transform(32719)
write_rds(regs_utm,'data/procesada/regs_utm_sf.rds')
#bbox de los límites de las regiones
bb_num <- regs_utm |>
sf::st_bbox()
# crear raster con resolución de 500m
r <- terra::rast(xmin = bb_num[1],
xmax = bb_num[3],
ymin = bb_num[2],
ymax=bb_num[4],
res =500,crs = "EPSG:32719")Calcular aspect y slope
elev_asp <- terra::terrain(elev_proj,'aspect')
elev_slope <- terra::terrain(elev_proj,'slope')
#unir las tres capas
elev_pred <- c(elev_proj,elev_asp,elev_slope)
#cambiar nombre a las capas
names(elev_pred) <- c("dem","aspect","slope")
#resamplea para ajustar a resolución de 500 m
elev_pred_res <- terra::resample(elev_pred,r)
#Mapa de los tres rasters
plot(elev_pred_res)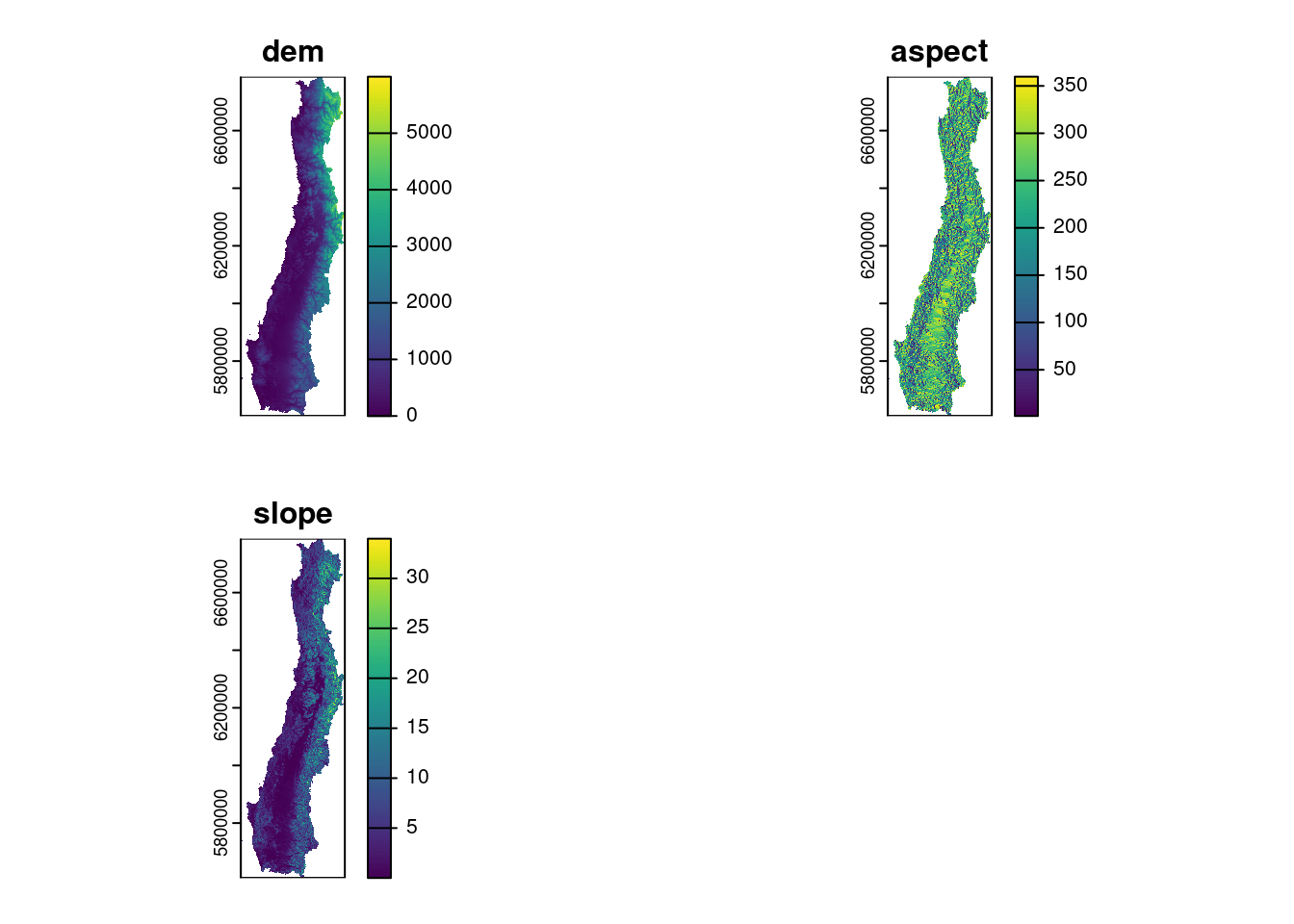
3.2 Crear raster de distancia a la costa
Descargar límites de Chile
lim_ch <- geodata::gadm('chile',level = 0,path = 'data/raw')
lim_chl <- lim_ch |>
sf::st_as_sf() |> #convierte en case sf
sf::st_geometry() |> #extrae solo la geometria
sf::st_transform(32719) #reproyecta a UTM WGS84 huso 19 Sur
plot(sf::st_geometry(lim_chl))
plot(sf::st_geometry(regs_utm),col='red',add = TRUE)
Extraer linea de costa
#simplifica poligono de límite de Chile y convierte a MULTILINESTRING
lim_chile_linea <- lim_chl |>
sf::st_simplify(dTolerance=1000) |>
sf::st_cast('MULTILINESTRING')
#simplifica poligono de límite de regiones y convierte a MULTILINESTRING
regs_linea <- regs_utm |>
sf::st_simplify(dTolerance=1000) |>
sf::st_cast('MULTIPOINT')
#intersecta limites regiones con límites de Chile
costa <- sf::st_intersection(regs_linea,lim_chile_linea)
# coordenadas para extraer polígono de la costa
m <- matrix(c(-70.511, -72.581, -74.759, -72.549,-70.511, -28.834, -39.706, -39.294, -28.575,-28.834),ncol=2)
#crear polígono
pol <- sf::st_polygon(list(m)) |>
sf::st_sfc(crs=4326) |>
sf::st_transform(32719)
#hace intersección para extraer linea de costa
costa <- sf::st_intersection(costa,pol) #linea de costaCalcula distancia a la costa
#extrae las coordenadas de cada pixel
xy <- terra::xyFromCell(r,1:ncell(r))
#convierte coordenadas en objeto sf
r_cent <- xy |>
tibble::as_tibble() |>
sf::st_as_sf(coords =c('x','y'),crs=32719)
#calcula distancia a la costa
dist_cost <- sf::st_distance(costa,r_cent)
#agregar distancias calculadas a raster r
values(r) <- as.numeric(dist_cost)
dcosta <- terra::mask(r,vect(regs_utm))
names(dcosta) <- 'dist_costa'
plot(dcosta)
plot(regs_utm,add=TRUE)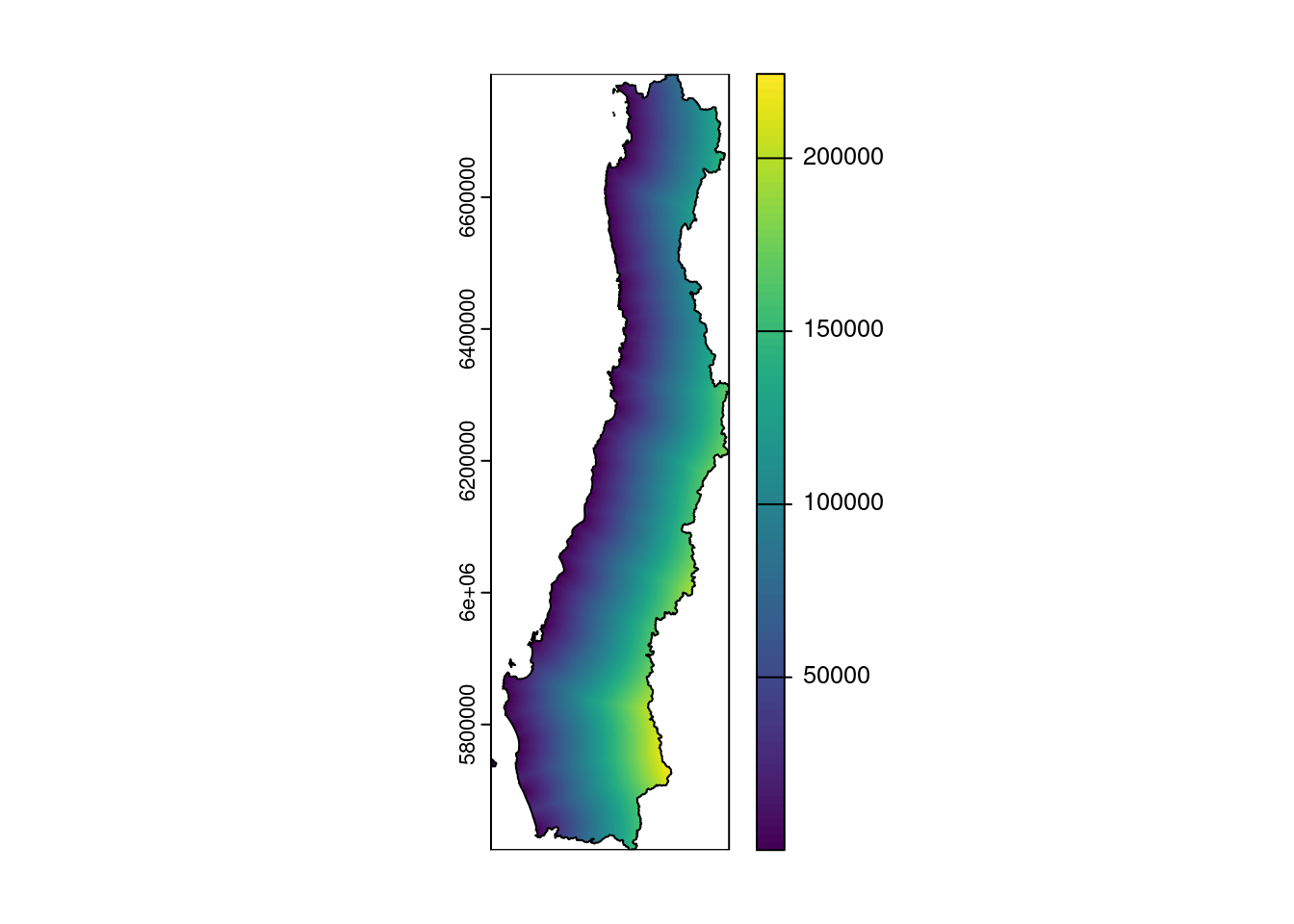
3.3 Descargar datos MODIS desde STAC cmr.earthdata.nasa.gov
De MODIS descargaremos del satelite TERRA los productos de temperatura superficial de suelo (LST) cada 8 días MOD11A2 version 6.1 y del índice NDVI mensual MOD13A3 versión 6.1. Ambos, con resolución espacial ~1km.
Para la descargar utilizaremos el repositorio cmr.earthdata.nasa.gov en donde están almacenados los Spatio Temporal Assets Catalogs (STAC). Para esto vamos a utilizar los paquetes {earthdatalogin} para las credenciales y {rsatc} para acceder y descargar los archvios necesarios.
# busca el producto MOD13A1 para enero del 2023
library(earthdatalogin)
earthdatalogin::edl_netrc() #login al servicio cmr.earthdata.nasa.gov
products <- c('MOD13A3.v061','MOD11A2.v061') #productos a descargar almacenados como carácter en un vector
mes <- 'enero' #mes de ejemplo que utilizaré para la descarga
o <- lapply(products,\(prod){ #itera sobre el vector products y le va asignanado a prod en cada iteración
items <- stac("https://cmr.earthdata.nasa.gov/stac/LPCLOUD") |> # indica la fuente del STAC
stac_search(collections = prod, #busca el producto prod, en la primera iteración corresponde a MOD13A3.v061
bbox = as.numeric(bb_num |> st_transform(4326)), #limite de la extensión donde buscar
datetime = "2023-01-01T00:00:00Z/2023-01-31T00:00:00Z") |> #fecha y hora para buscar, en este caso para el mes de enero
post_request() |>
items_fetch()
items$features |> #indica los items a descargar
purrr::map(list("assets",6,'href')) |> #extrae el url del producto
purrr::map_chr(\(x) edl_download(x,dest = file.path('data/raw/modis/',prod,mes,basename(x)))) #realiza la descarga en la carpeta indicada
})Leer los archivos descargados. En este caso para cubrir el área de estudio (Coquimbo-Araucania) se requieren tres tiles de MODIS ‘h11v11’,‘h11v12’y ’h12v12’. En el caso del producto MOD13A3 que es mensual, se tienen tres archivos, uno por cada tile. En el caso del producto MOD11A2 que tiene frecuencia de 8 días, se tienen 4 archivos, uno para cada tile. Cada uno de los productos tiene varias bandas, en este caso NDVI y LST, se encuentran en la primera banda.
Con NDVI de MOD13A3 hay que hacer un mosaico con los tres tiles del mes de enero.
# MOD13A3 NDVI Enero
files <- list.files('data/raw/modis/MOD13A3.v061/enero',full.names = TRUE) #lista los archivos guardados para enero
ndvi_ene <- files |>
purrr::map(rast,lyrs=1) |> #itera y carga cada archivo y los almacena en una lista
terra::sprc() |> # crea una spatRasterCollection para poder hacer el mosaico
terra::mosaic() |> #crea el mosaico
terra::project('EPSG:32719') |> #reproyecta a UTM
terra::mask(vect(regs_utm)) |> #aplica mascara para el área de estudio
terra::trim() |> #elimina los NA sobrantes alrededor de la extensión
terra::app(\(x) x*1e-8) # transforma los valorea al rango 0-1
ndvi_ene <- terra::resample(ndvi_ene,r) #resamplea para igual resolución
names(ndvi_ene) <- 'ndvi_ene' #cambia nombre
plot(ndvi_ene)
plot(regs_utm,add = TRUE)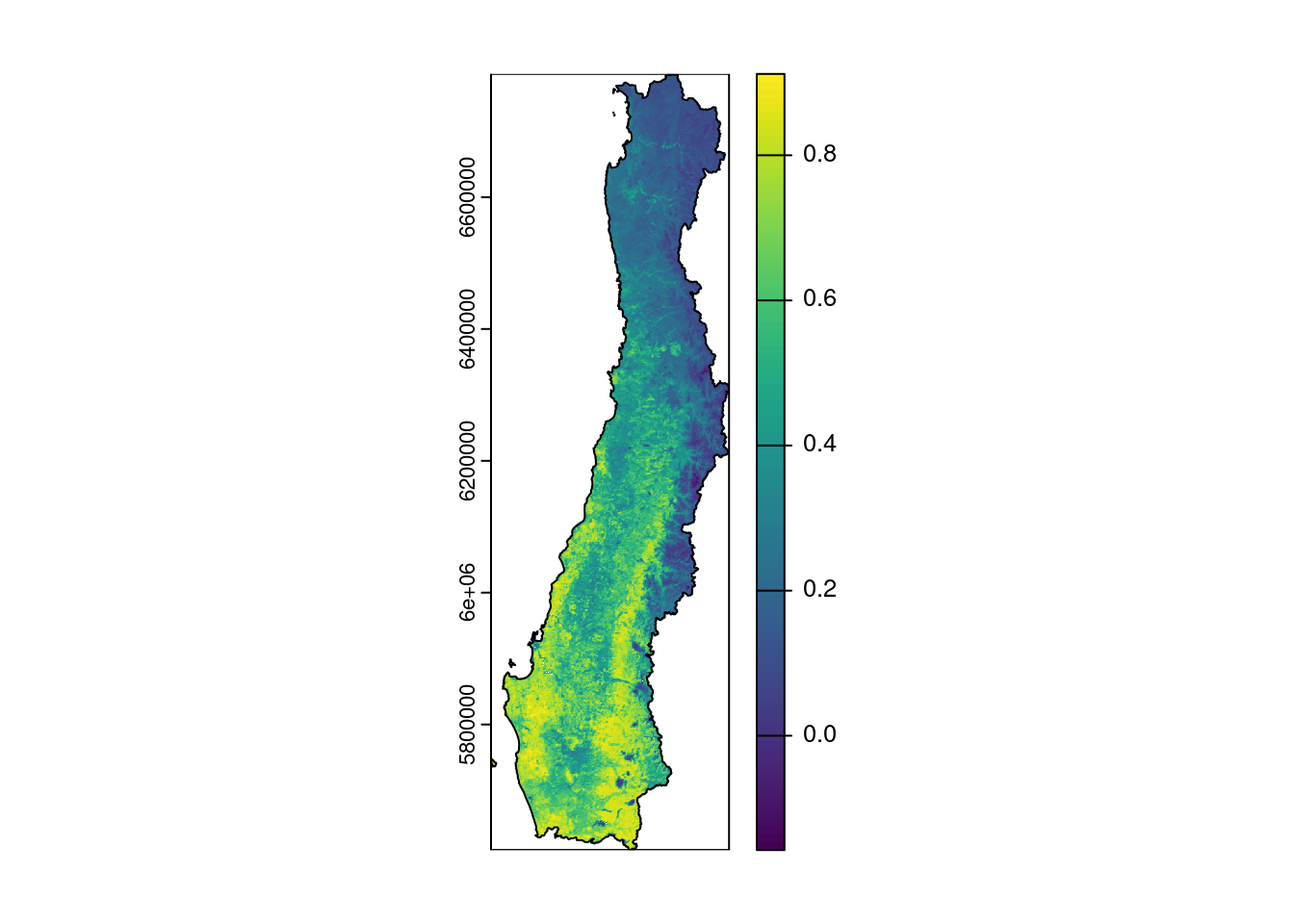
Con LST de MOD11A2, es necesario promediar las cuatro fechas y luego hacer el mosaico con los tres tiles resultantes.
Calculo del promedio para cada tile y el resultado se almacena en una lista
# MOD11A2 LST Enero
tiles <- c('h11v11','h11v12','h12v12') #tiles que corresponden al área de estudio
lst_out <- purrr::map(tiles,\(tile){
files <- list.files('data/raw/modis/MOD11A2.v061/enero',full.names = TRUE,pattern = tile)
lst_regs <- files |>
purrr::map(rast,lyrs = 'LST_Day_1km') |> #extrae la banda por el nombre, también se podría haber usado el índice (1)
terra::rast() |>
terra::app(mean)
})Mosaico para los tres tiles resultantes.
lst_ene <- lst_out |>
terra::sprc() |> # crea una spatRasterCollection para poder hacer el mosaico
terra::mosaic() |> # aplica el mosaico para unir los tres tiles
terra::project("EPSG:32719") |> #reproyecta a UTM
terra::mask(vect(regs_utm)) |> #aplica mascara para el área de estudio
terra::trim() |> #elimina NA sobrantes en los bordes
terra::app(\(x) x-273.15) #convierte la T° de Kelvin a °CResampleo para igualar la resolución espacial con los otros predictores.
lst_ene <- resample(lst_ene,r)
names(lst_ene) <- 'lst_ene'
plot(lst_ene)
plot(regs_utm,add = TRUE)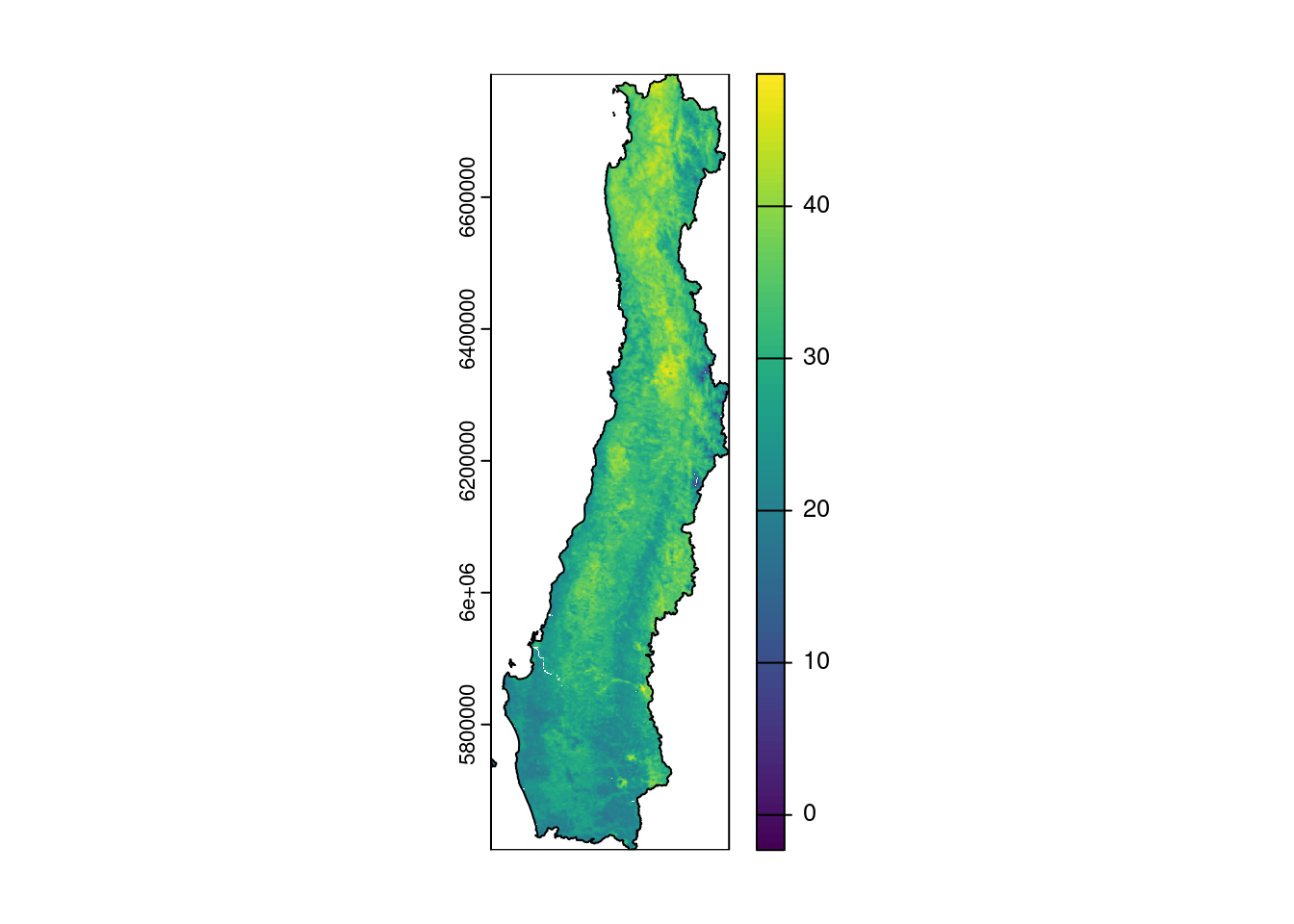
3.4 Todos los predictores raster
Se juntan todos los predictores en un objeto spatRaster y se guarda en el disco.
predictores <- c(elev_pred_res,dcosta,ndvi_ene,lst_ene)
writeRaster(predictores,'data/procesada/predictores_enero.tif',overwrite = TRUE) #guarda los predictores
plot(predictores)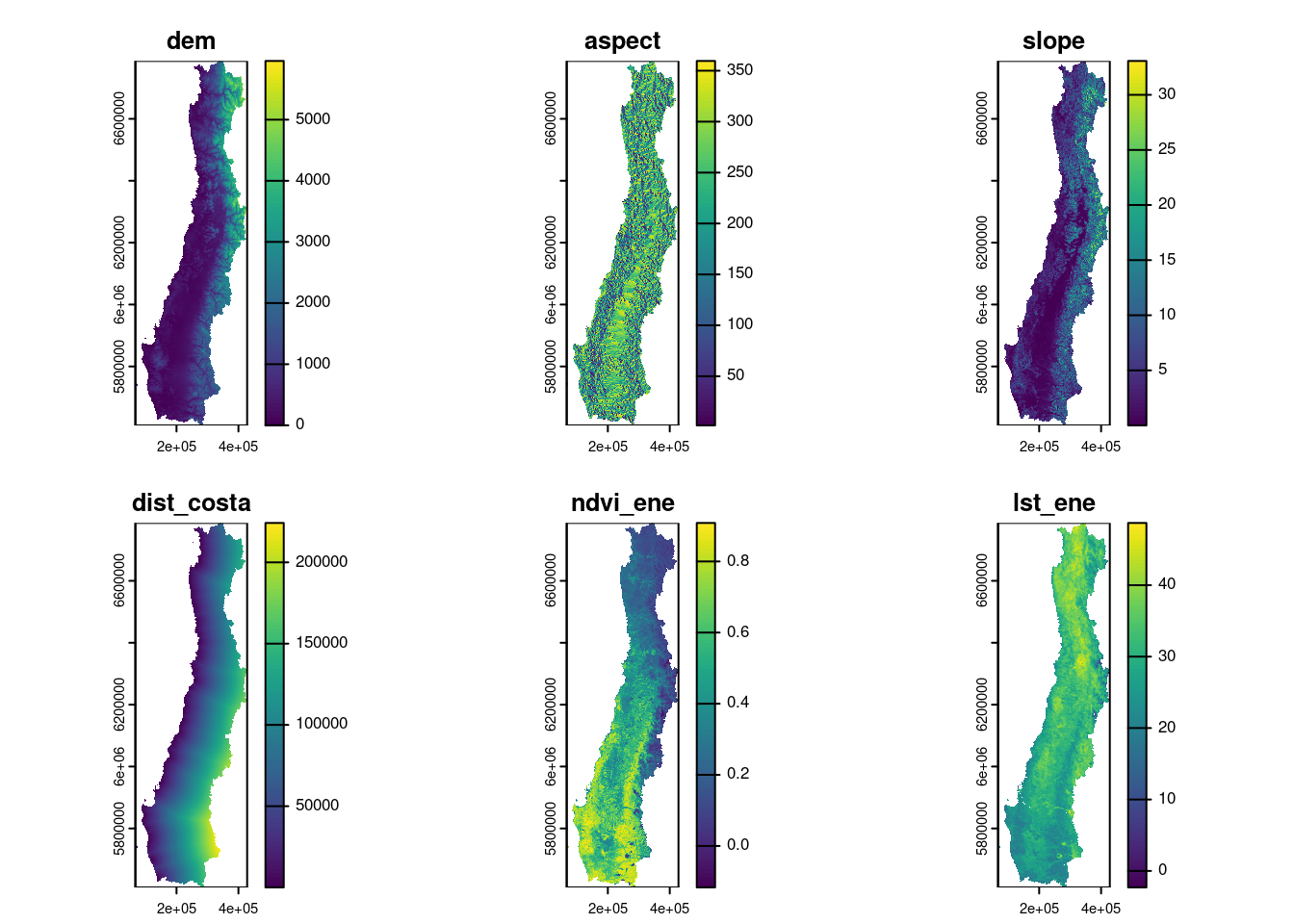
4 Preparar datos in-situ temperatura
Datos de las estaciones agromet
estaciones_agromet |> glimpse()Rows: 417
Columns: 8
$ ema <dbl> 1, 2, 3, 4, 5, 6, 7, 8, 9, 10, 11, 12, 13, 14, 15, 16, 1…
$ institucion <chr> "FDF", "FDF", "FDF", "FDF", "FDF", "FDF", "FDF", "FDF", …
$ nombre_ema <chr> "Azapa1", "Azapa2", "Tranque Lautaro", "Jotabeche", "Hor…
$ comuna <chr> "Arica", "Arica", "Tierra Amarilla", "Tierra Amarilla", …
$ region <chr> "Arica y Parinacota", "Arica y Parinacota", "Atacama", "…
$ latitud <dbl> -18.50964, -18.52044, -27.97558, -27.58861, -27.72889, -…
$ longitud <dbl> -70.24806, -70.23267, -70.00000, -70.24472, -70.19667, -…
$ fecha_de_alta <dttm> 2013-03-08 06:49:10, 2013-03-08 06:49:10, 2013-03-08 06…Transformamos el tibble en un objeto sf
estas_sf <- estaciones_agromet |>
st_as_sf(coords = c('longitud','latitud'),crs = 4326) |> #crea objeto sf
st_transform(32719) #reproyecta a UTM WGS84 huso 19 SurSeleccionamos las estaciones que se encuentran en nuestra área de estudio
estas_regs <- st_intersection(estas_sf,regs_utm) #intersección estaciones con área de estudioWarning: attribute variables are assumed to be spatially constant throughout
all geometriesids <- estas_regs |> pull(ema) #extrae la columna ema de las estacionesCargar datos meteorológicos de las estaciones agromet para el año 2023 y muestra un resumen.
data_agro <- read_rds('data/raw/agromet/datos_agromet_2023.rds')
data_agro |> glimpse()Rows: 3,651,647
Columns: 13
$ station_id <dbl> 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, …
$ fecha_hora <dttm> 2023-01-01 00:00:00, 2023-01-01 01:00:00, 2023-…
$ temp_promedio_aire <dbl> NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, …
$ precipitacion_horaria <dbl> NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, …
$ humed_rel_promedio <dbl> NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, …
$ presion_atmosferica <dbl> NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, …
$ radiacion_solar_max <dbl> NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, …
$ veloc_max_viento <dbl> NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, …
$ temp_minima <dbl> NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, …
$ temp_maxima <dbl> NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, …
$ direccion_del_viento <dbl> NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, …
$ grados_dia <dbl> 425.75, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, …
$ horas_frio <dbl> NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, …Función que realiza un filtro de valores anómalos usando un z-score modificado con la mediana.
filt_out2 <- function(x,c,...){
M <- .6745*(x - median(x,...))/mad(x,...)
x[M > c] <- NA
x[M < -c] <- NA
return(x)
}Filtramos los datos de temperatura para las estaciones en el área de estudio y promediamos para los meses en estudio
data_agro_estaciones <- data_agro |>
filter(station_id %in% ids) |> #filtra estaciones que corresponden a ids
select(station_id,fecha_hora,temp_promedio_aire) |> #selecciona las columnas indicadas
mutate(temp_promedio_aire = filt_out2(temp_promedio_aire,c=1.7)) |> #aplica filtro simple para outliers
mutate(mes = month(fecha_hora)) |> # crea una variable mes
filter(mes %in% c(1,5,9,12)) |> #filtra los meses
group_by(station_id,mes) |> # agrupa por codigo de estación y mes
summarize(temp = mean(temp_promedio_aire,na.rm = TRUE)) |> #calcula el promedio mensual
drop_na() #elimina las filas que tienen valores NA`summarise()` has grouped output by 'station_id'. You can override using the
`.groups` argument.Realizamos la unión con el objeto sf de las estaciones
data_estas_sf <- estas_regs |>
select(ema) |>
dplyr::rename(station_id = ema) |>
left_join(data_agro_estaciones) Joining with `by = join_by(station_id)`4.1 Breve analisis exploratorio
data_estas_sf |>
st_drop_geometry() |>
ggplot(aes(temp)) +
geom_density() +
theme_bw()Warning: Removed 32 rows containing non-finite outside the scale range
(`stat_density()`).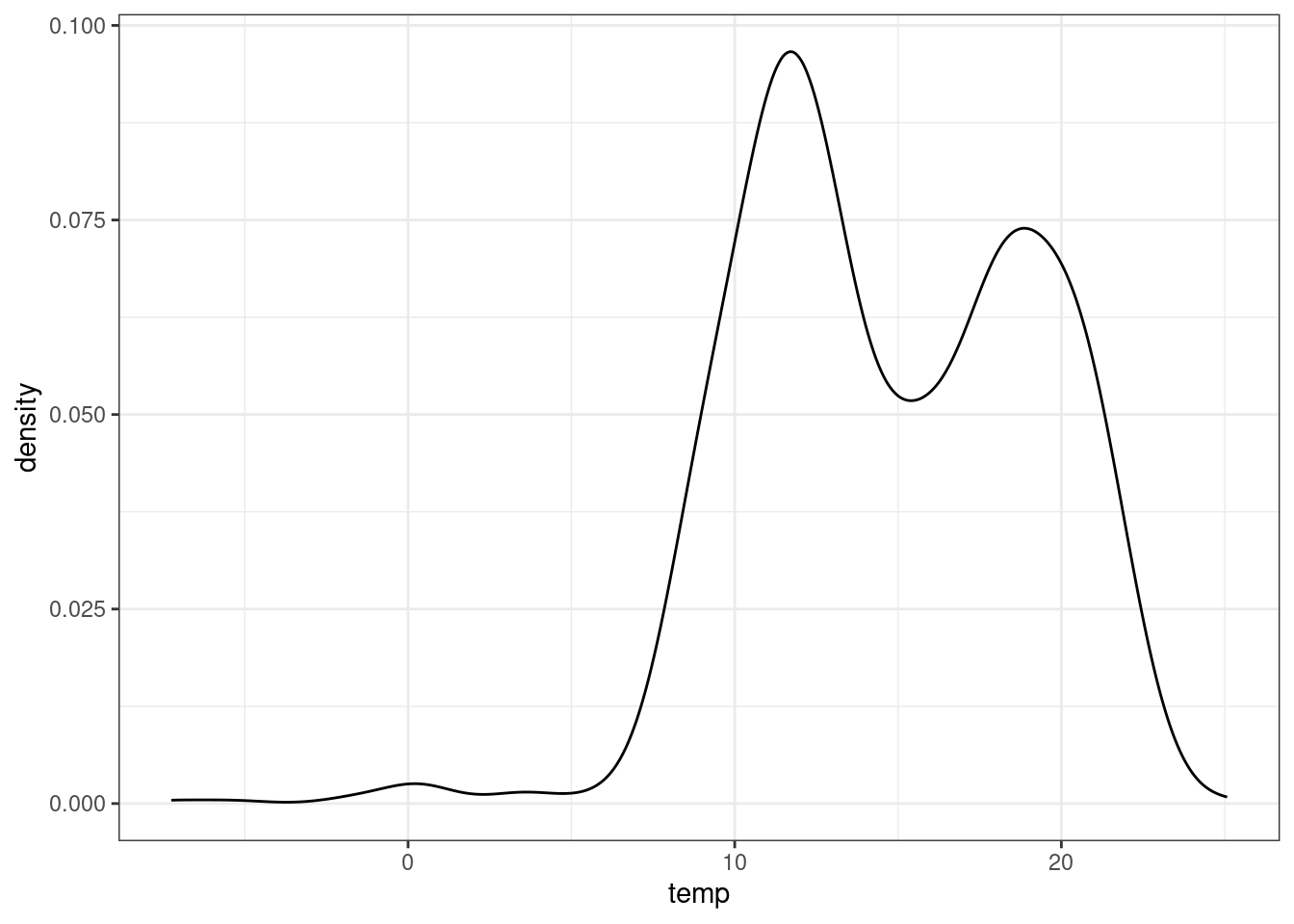
data_estas_sf |>
cbind(st_coordinates(data_estas_sf |> st_transform(4326))) |>
st_drop_geometry() |>
ggplot(aes(temp,Y)) +
geom_point() +
theme_bw()Warning: Removed 32 rows containing missing values or values outside the scale range
(`geom_point()`).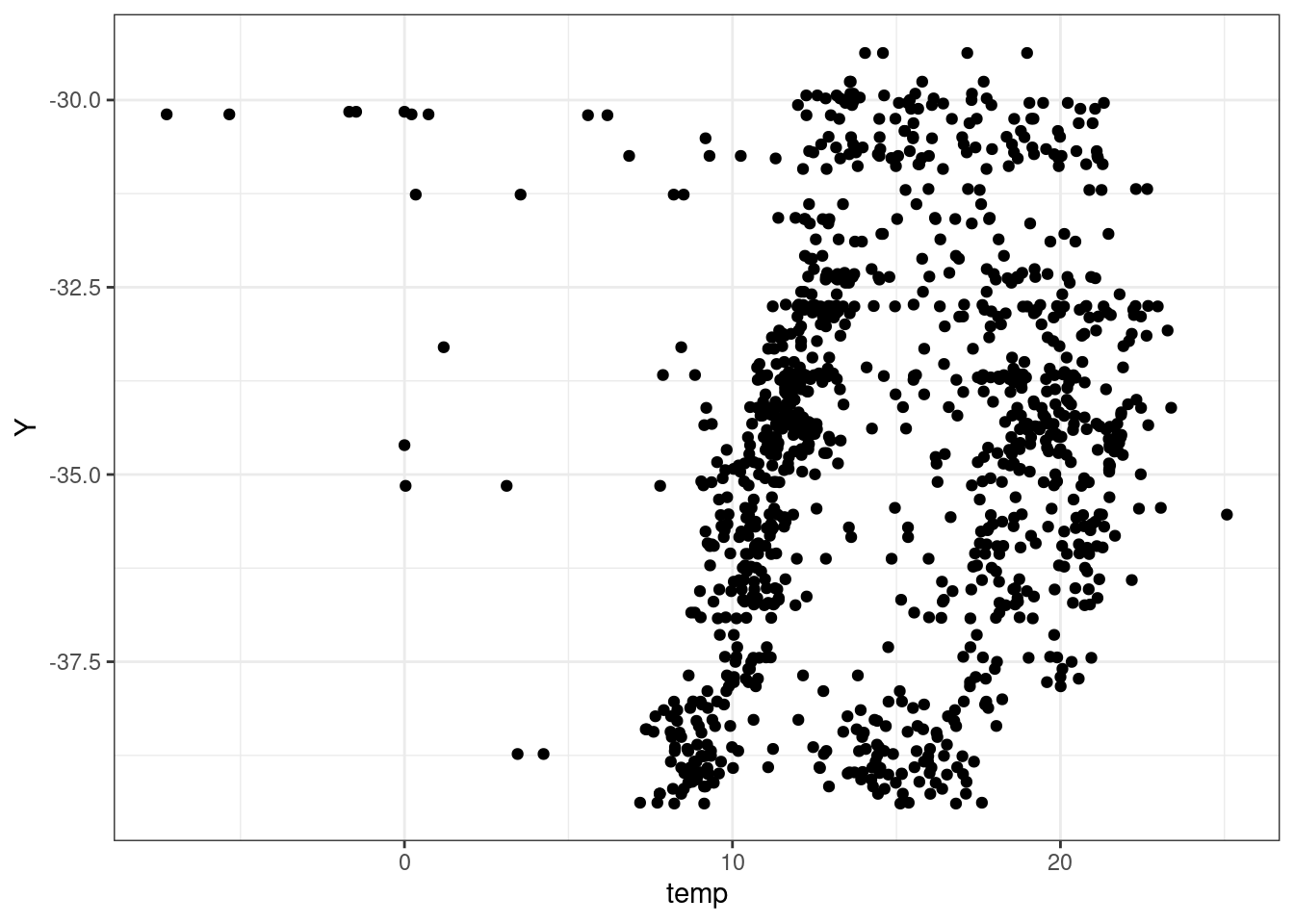
5 Mapeo de predictores raster y datos de temperatura
Enero 2023
tmap_mode('view')tmap mode set to interactive viewingpreds <- rast('data/procesada/predictores_enero.tif')
tm_shape(preds) +
tm_raster(style = 'cont') +
tm_shape(data_estas_sf |> filter(mes == 1)) +
tm_dots(col='temp',style = 'jenks',palette = viridis::viridis(10)) +
tm_facets(free.scales.fill = TRUE,as.layers = FALSE) +
tm_layout(legend.show = FALSE)stars object downsampled to 553 by 1806 cells. See tm_shape manual (argument raster.downsample)Tip: rasters can be shown as layers instead of facets by setting tm_facets(as.layers = TRUE).Variable(s) "NA" contains positive and negative values, so midpoint is set to 0. Set midpoint = NA to show the full spectrum of the color palette.6 Crear set de datos para modelación espacial
#extrae los datos de los predictores en las ubicaciones de las estaciones
data_temp_pred <- terra::extract(predictores,data_estas_sf)
#une con los datos de temperatura in-situ
data_unida <- cbind(data_estas_sf,data_temp_pred) |>
select(-ID) |>
drop_na()
#almacena en el disco el resultado
write_rds(data_unida,'data/procesada/data_estas_temp_con_predictores.rds')
#crea una tabla dinámica con {gt}
library(gt) #pquete para la creación de tablas
data_unida |>
sf::st_drop_geometry() |>
gt::gt() |>
gt::fmt_number(decimals = 1, drop_trailing_zeros = TRUE) |>
gt::opt_interactive()